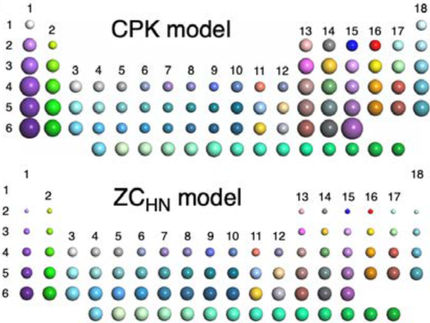
Der Computer als Super-Mikroskop für lebenswichtige Moleküle
Wie Computerchemie die Medizin weiterbringt
Die Computerchemikerin Sereina Riniker hat den Latsis-Preis der ETH Zürich gewonnen. Ausgezeichnet wird sie für die Entwicklung neuer Methoden, mit denen sich Molekülbewegungen simulieren lassen.
Wer die Grundlagen des Lebens bis ins Kleinste verstehen will, kommt an den Atomen nicht vorbei. Zellen sind aus Molekülen aufgebaut, und diese wiederum aus Atomen. In ihrer Forschung untersucht die ETH-Professorin Sereina Riniker, wie sich Moleküle auf atomarer Ebene bewegen, und welche Eigenschaften und Wirkungen die Moleküle dadurch besitzen. Auf der Grundlage ihrer Forschungsergebnisse lassen sich zum Beispiel die Eigenschaften möglicher Wirkstoffe für Medikamente verbessern.
Für ihre Arbeit auf dem Forschungsgebiet der computergestützten Chemie hat Sereina Riniker den Latsis-Preis 2018 der ETH Zürich erhalten, der wissenschaftlich herausragende Arbeiten von ETH-Forschenden, die jünger als 40 Jahre alt sind, honoriert. Die Auszeichnung wird traditionsgemäss am ETH-Tag gewürdigt. «Diese Ehrung ist eine willkommene Überraschung und Unterstützung für meine grundlagen- und theoriebezogene Forschung», sagt Sereina Riniker.
Wie Computerchemie die Medizin weiterbringt
Die Arbeitsgruppe von Sereina Riniker ist bekannt für ihre innovativen Ansätze, um die Eigenschaften von zyklischen Peptiden, einer speziellen Gruppe von Eiweissmolekülen mit zyklischer Struktur, zu erforschen. Diese Klasse von Verbindungen ist von grossem Interesse in der Medizin, da zyklische Peptide zum Beispiel das Potential haben, Wechselwirkungen zwischen Proteinen zu hemmen.
Eine Voraussetzung für ihren Einsatz als Wirkstoff ist, dass sie sich durch die Zellmembran hindurchbewegen können, um so das Zellinnere zu erreichen und dort ihre Wirkung entfalten zu können. Die Überwindung der Zellmembran ist jedoch wegen der Grösse der Peptide nicht immer einfach.
Am Computer untersucht Riniker, warum bestimmte Arten zyklischer Peptide leichter und schneller durch eine Zellmembran hindurchgehen als andere. Die Ergebnisse dieser Forschung können eine Grundlage für die Optimierung neuer Wirkstoffe darstellen.
Von der klassischen Physik zum Supercomputer
In der Laudatio des diesjährigen Latsis-Preises der ETH heisst es: «Als Computerchemikerin entwickelt Sereina Riniker Algorithmen, die es ermöglichen, der Bewegung von Atomen in komplexen molekularen Gruppen zu folgen und daraus quantitative Daten zu gewinnen.» Zudem habe sie die Hauptprobleme klassischer Simulationen ermittelt, die lange eine chemisch und physikalisch fundierte Untersuchung der Dynamik kleiner Biomoleküle behindert hätten.
Tatsächlich baut Riniker die rechnerische Modellierung der atomaren Bewegungen auf den physikalischen Bewegungsgesetzen auf, die Isaac Newton (1642-1726) in die Mechanik einführte. Die nötigen Berechnungen sind sehr aufwendig und erfordern den Einsatz von Computerclustern.
Zu den grossen Herausforderungen gehören die schiere Zahl der Wechselwirkungen und die extrem kurzen Zeiteinheiten: Um die Atombewegungen zu berechnen, wird die Bewegung in einzelne Schritte unterteilt, von denen jeder eine winzige Femtosekunde kurz ist, das heisst 0.000 000 000 000 001 oder 10-15 Sekunden. Die Zeitschritte müssen so kurz sein, um den Berechnungsfehler klein zu halten. Entsprechend viele Zeitschritte sind zu berechnen, um experimentell relevante Zeiträume zu erreichen.
Ein Monat für eine Simulation
Neben der zeitlichen Dimension bestimmt die Anzahl der Atome im System die Komplexität der Berechnung. Kleine Moleküle wie zum Beispiel die zyklischen Peptide bestehen aus wenigen hundert Atomen. Grosse Moleküle wie die Proteine umfassen mitsamt dem umgebenden Wasser 10'000 bis 100'000 Atome. Daraus ergeben sich für eine einzige Simulation mehr als 100 Millionen Wechselwirkungen, die in jedem einzelnen Schritt zu berechnen sind.
Selbst modernste Computercluster, wie der Hochleistungs-Rechner der ETH oder das nationale Rechenzentrum CSCS in Lugano, benötigen für die Simulation der Bewegung eines zyklischen Peptids über den Zeitraum von einer Mikrosekunde rund einen Monat. Die Zeitspanne mehrerer Mikrosekunden ist notwendig, um die Bewegungen eines Peptids ausreichend zu beschreiben. Am Computer wird eine Vielzahl von möglichen Veränderungen durchgerechnet, sodass man aus der Menge der Möglichkeiten herausfinden kann, wie Veränderungen die Eigenschaften der Peptide beeinflussen. Die Erkenntnisse der Simulation werden danach im Labor experimentell überprüft.
Ergänzende Einsichten zu Experimenten im Labor
Die Simulation am Computer ersetzt die experimentelle Forschung im Labor somit nicht, sondern sie ergänzt sie: Eine Simulation von grösseren Molekülen zum Beispiel baut auf experimentellen Daten auf. «Dank der Computermethoden haben wir eine Art Mikroskop, das uns erlaubt, die molekulare Dynamik auf atomarer Ebene und für einzelne Moleküle zu betrachten. Das ist mit anderen Methoden nicht möglich», sagt Riniker. «Mit den Simulationen können wir die experimentellen Ergebnisse zu einem Gesamtbild vervollständigen.»
Um komplexe Themen wie die Eigenschaften von zyklischen Peptiden durch Simulationen erforschen zu können, sind spezialisierte Computerprogramme notwendig. Diese entwickelt die Arbeitsgruppe von Sereina Riniker selber. Zudem braucht es detaillierte Kenntnisse aus verschiedenen Bereichen der Naturwissenschaften, was sich an der interdisziplinären Zusammensetzung der Arbeitsgruppe von Riniker zeigt, in der Studenten, Doktoranden und Postdoktoranden aus Chemie, Physik, Biologie sowie Informatik eng zusammenarbeiten und sich regelmässig austauschen. «Forschung ist Teamarbeit», sagt Sereina Riniker abschliessend.